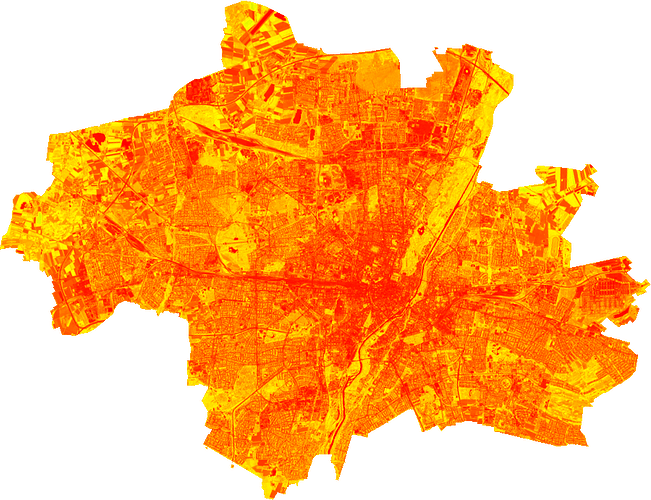
Hey Leute,
ich spiele gerade mit Satellitendaten rum und möchte unter anderem das Stadtgebiet München aus einer GeoTIFF-Aufnahme herausschneiden – das klappt soweit auch, indem ich rasterio.mask() nutze. Allerdings möchte ich, dass der Bereich außerhalb der Stadt transparent ist und nicht so ![]() aussieht
aussieht
Das Problem (so wie ich es einschätze) liegt logischerweise darin, dass numpy-Arrays nur die Form eines Tensors annehmen können und die Stadt München leider davon abweicht bzw. dass irgendein Wert, im Falle von GeoTIFF der nodata-Wert, bei mir nodata = 0 (damit hast du nicht gerechnet, stimmt’s? :P), verwendet werden muss, um die Bereiche aufzufüllen, von dem ich nicht annehmen kann, dass er in meiner Geometrie nicht vorkommt, weshalb ich ihn nicht einfach herausfiltern kann. Oder anders gesagt: Wenn ich alles, was nodata/0 entspricht filtere, können Lücken innerhalb des Stadtgebietes auftreten, was ich vermeiden möchte.
Die Metadaten (auch wenn nicht alle für meine Frage notwendig sind) des Bildes lauten:
{
'driver': 'GTiff',
'dtype': 'uint16',
'nodata': 0.0,
'width': 7711,
'height': 7821,
'count': 1,
'crs': CRS.from_epsg(32632),
'transform': Affine(30.0, 0.0, 574785.0, 0.0, -30.0, 5532615.0)
}
Mir fallen zwar ein bis zwei Workarounds ein, bspw. dtype ändern, nodata < 0 verwenden, Form herausschneiden, nodata filtern/transparent setzen, dytpe auf Ursprungswert legen, aber schöner wäre natürlich eine direkte/konkrete Lösung. Vielleicht muss man auch den dtype ändern, nodata < 0 verwenden, die Form herausschneiden, Transparenz eif
Deswegen möchte ich euch um Vorschläge bitten. ![]()
Das FSI-Forum kann keine (Geo)TIFF-Dateien verarbeiten, falls ihr mit dem Bild selbst herumexperimentieren möchtet.